理化学研究所(理研)バイオリソース研究センター 微生物材料開発室の加藤 真悟 上級研究員、大熊 盛也 室長、環境資源科学研究センター 植物免疫研究グループの増田幸子研究員、白須 賢 グループディレクターらの研究チームは、国際的な微生物株[1]保存機関である微生物材料開発室(JCM[2])が保有する原核生物(細菌およびアーキア(古細菌))株のうち、系統学的にも生理学的にも多様な351株の全ゲノム配列を解読しました。
本研究の成果は、信頼性の高い分類体系の確立に貢献するだけでなく、未知の機能遺伝子や新規の代謝経路の探索を加速させ、環境・健康・食・エネルギーといった幅広い研究分野の基盤となると期待されます。
今回、研究チームは、JCMが保有・公開している約2万株の中から、種を代表する基準株や、技術的に培養の難しい株を中心に、351株の全ゲノム解読を実施しました。そのうちの200株以上においては、これまで全ゲノム配列が決定されていない株でした。ゲノム解読の結果、分類学的な再考が必要な株、未知の染色体外DNA[3]を有する株、新規もしく未検証の代謝機能を有する可能性のある株などが見つかりました。今回解読したゲノム配列は、すべて公共データベースで公開しています。
本研究は、科学雑誌『Genome Research』オンライン版(4月7日付)に掲載されました。
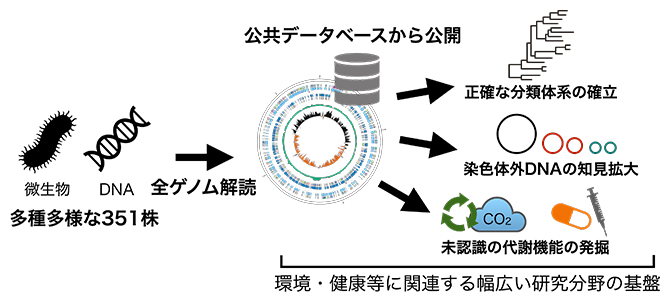
本研究の概要
背景
生命の設計図ともいえるゲノムは、さまざまな生命科学研究において不可欠な基盤情報です。近年の塩基配列決定技術の急激な進歩と相まって、すでに数多くの生物の全ゲノム配列が決定されています。特に、ゲノムの構造が単純でサイズも小さい原核生物においては、種の代表となる基準株のゲノムが複数の国際的な大規模ゲノムプロジェクトによって優先的に決定されてきました。しかしながら、酸素に触れると死滅してしまう絶対嫌気性であったり、増殖速度が著しく遅かったりする、いわゆる「難培養」の多くの株は、基準株であったとしても、そのゲノム配列が決定されないまま残されていました。国際的な微生物株保存機関であるJCMにおいても、そういったゲノム未解読もしくは粗解読の難培養性基準株を多数保有していました。ゲノム情報が整備されていないと、研究材料として利用されにくく、結果として新たな生物学的発見の機会が失われてしまいます。
研究手法と成果
そこで研究チームは、JCMが保有するゲノム未解読もしくは完成度の低い粗解読の状態の原核生物351株(細菌290株とアーキア61株)を対象に、最先端のロングリードおよびショートリードDNAシーケンサー[4]を駆使して、全ゲノム解読を実施しました(図1)。この351株には、基準株が284株含まれており、また絶対嫌気性メタン生成アーキアなどの難培養株も多く含まれています。351株のうち、203株は実際に培養してDNAを抽出し、残りの148株は理研バイオリソース研究センター遺伝子材料開発室と共同で過去に培養・抽出してリソースとして整備されたDNAを活用して、それぞれシーケンサーで解読しました。
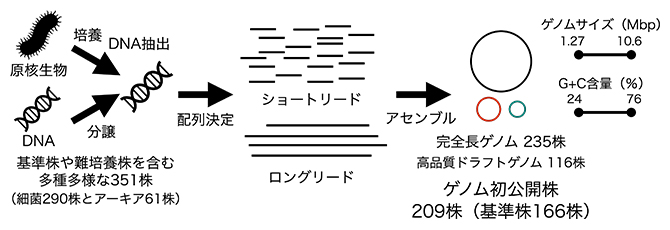
図1 原核生物351株の全ゲノム解読
JCMが保有する351株を対象に、203株は実際に培養してDNAを抽出し、残りの148株は理研バイオリソース研究センター遺伝子材料開発室と共同で過去に培養・抽出したDNAを活用して、それぞれロングリードおよびショートリードDNAシーケンサーシーケンサーで解読した。得られたロングリードおよびショートリードのDNA配列をつなぎ合わせ、完全長もしくは高品質ドラフトゲノム配列を決定した。
その結果、235株(基準株189株)で完全長ゲノム配列を決定することができ、残りの株についても高品質ドラフトゲノム(全ゲノムの概要)配列を決定することができました。209株(基準株166株)においては、これまでにゲノム配列が全く公開されていない株でした(2025年4月配列登録時)。決定したゲノムのサイズは1.27Mbp(M:100万、bp:塩基対)から10.6Mbp、GC含量(グアニン(G)とシトシン(C)の割合)は24%から76%であり、既知の原核生物ゲノムの値の範囲内でした。
本研究の351株の全ゲノム解読により、分類学、分子生物学、さらには生理学的な新しい知見が数多く得られました(図2)。
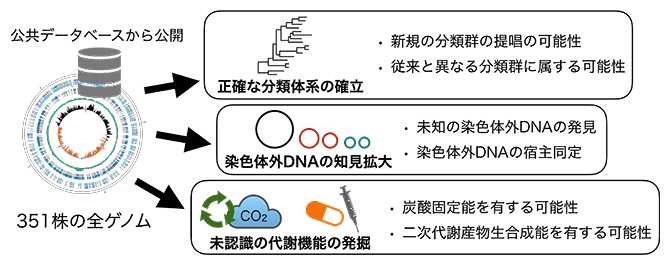
図2 全ゲノム解読から得られた成果
今回解読した351株の全ゲノム配列は、全て公共データベースに登録し、一般に公開した。全ゲノム解読の結果、さまざまな新しい知見を得ることができた。
全ゲノム配列を用いた系統解析は、現在の微生物分類学において有力な手法の一つです。本研究で初めてゲノム配列が解読された株において、これまで曖昧であった系統学的位置が明確になりました。中には、新しい高次分類群(「科(family)」、「目(order)」、さらには「綱(class)」)を提案できる可能性がある株や、新種として新たに提唱される可能性のある株、さらに従来とは異なる分類群に属する可能性のある株が見つかりました。これらの候補株は、今後のより詳細な系統学的および生理学的特性解析によって、より正確な分類体系が確立する可能性があります。
微生物株の全ゲノム配列を決定することの強みの一つは、その株がプラスミドなどの染色体外DNAを持っているかどうかが分かることです。本研究では、162個の環状染色体外DNAが見つかり、そのサイズは1.8kbp(k:1,000、bp:塩基対)から1.4Mbpとかなりの幅があることが分かりました。注目すべきは、それらの環状染色体外DNAの中には、プラスミドなどを検出する既存のソフトウエアでは同定されないような新規の配列が含まれていた点です。このように、本研究で構築したゲノムデータセットは、染色体外DNAの多様性と機能に関する従来の知見を拡大すると期待されます。
ゲノムにコードされている遺伝子を調べることで、その微生物が有する代謝機能を推定することができます。本研究では、環境・健康の研究に直結する炭酸固定[5]や二次代謝産物[6]生合成に関与する遺伝子を詳しく調べました。その結果、炭酸固定に関しては、60株以上で関連遺伝子が見つかり、中には炭酸固定能がまだ実証されていない株も含まれていました。さらに、炭酸固定能があると報告されている複数の株において、既知の関連遺伝子が見つからず、未知の炭酸固定経路を持つ可能性が示唆されました。二次代謝産物の生合成に関しては、従来の報告通り放線菌[7]株から多く関連遺伝子が検出されました。その一方で、これまであまり研究が進んでいない絶対嫌気性細菌やアーキアにおいても二次代謝産物の生合成に関わる遺伝子が検出され、新たな二次代謝産物の探索における研究対象になる可能性があります。
今後の期待
本研究の強調すべき点は、「培養可能な微生物株」の全ゲノムを解読し、その配列情報を公共データベース注)に公開したということです。近年のコンピューターと情報解析技術の飛躍的な進歩に伴い、ゲノム情報から実世界で起こる生命現象を予測し(例えばタンパク質の立体構造予測)、新たな知見の創出や技術開発へ展開する研究が急速に広まっています。本研究で解読したゲノム配列は、そのような情報解析の基盤となります。予測した生命現象の妥当性を確かめるためには、実験による検証が不可欠です。今回ゲノム解読をした微生物株は全て、一般の研究者が利用可能なリソース(=実験材料)としてJCMで整備されています。本研究により、微生物リソースの付加価値が高まり、その利活用が促進されることで、環境・健康・食・エネルギーといった幅広い生命科学分野における基礎および応用研究の発展に貢献すると期待されます。
補足説明
- 1.微生物株
純粋培養物として維持・継代された単一系統の細胞集団。 - 2.JCM
国際的な微生物株保存機関の一つ。微生物材料開発室は、JCMとして発足し、1981年より微生物株の収集・保存・品質管理・提供を行う微生物系統保存事業を実施している。現在では、世界有数の規模を誇る微生物コレクションとして、研究や産業利用の基盤となる微生物株を保存・提供するとともに、ゲノム情報や培養情報の整備を進めている。JCMはJapan Collection of Microorganismsの略。 - 3.染色体外DNA
細胞に含まれるDNAの中で、染色体以外のプラスミドやウイルスなどのDNA。 - 4.ロングリードおよびショートリードDNAシーケンサー
数万塩基対以上の長いDNA断片もしくは数百塩基対程度の短いDNA断片を、それぞれ読み取ることができる装置。両シーケンサーから得られたデータを合わせて解析することで、より高品質のゲノム配列が決定できる。 - 5.炭酸固定
CO2(二酸化炭素)からバイオマス(有機化合物)をつくり出す代謝反応。炭素固定やCO2固定などともいう。CO2などの温室効果ガスの排出量と吸収量の収支をゼロにする脱炭素社会の実現を目指す上で注目されている。 - 6.二次代謝産物
生物の生存に必須である糖、有機酸、アミノ酸、脂質などの一次代謝産物以外の、多様な構造・機能を持つ有機化合物の総称。例として抗生物質が挙げられ、医薬品として用いられている。 - 7.放線菌
土壌中など自然界に広く存在するグラム陽性の真正細菌であり、複雑な構造を持つ二次代謝産物を生産する。人類は、それらの中から、医薬、農薬、動物薬などの生理活性を持つ物質を利用してきた。医薬探索源として重要視されている。
研究チーム
理化学研究所
バイオリソース研究センター 微生物材料開発室
上級研究員 加藤 真悟(カトウ・シンゴ)
特別嘱託研究員(研究当時)伊藤 隆(イトウ・タカシ)
(現 業務アドバイザー)
専任研究員 坂本 光央(サカモト・ミツオ)
室長 大熊 盛也(オオクマ・モリヤ)
環境資源科学研究センター 植物免疫研究グループ
研究員 増田 幸子(マスダ・サチコ)
テクニカルスタッフⅡ 柴田 ありさ(シバタ・アリサ)
グループディレクター 白須 賢(シラス・ケン)
研究支援
本研究は、ナショナルバイオリソースプロジェクト(NBRP)中核的拠点整備プログラム「ゲノム情報等整備」の研究課題「難培養性原核生物の基準株の完全長ゲノム情報整備(研究代表者:大熊盛也)」、科学技術振興機構(JST)革新的GX技術創出事業GteX「バイオものづくり」領域の研究課題「先端的植物バイオものづくり基盤の構築(研究代表者:大熊盛也、JPMJGX23B0)」「GXを駆動する微生物・植物『相互作用育種』の基盤構築(研究代表者:野村暢彦、JPMJGX23B2)」、日本学術振興会(JSPS)科学研究費助成事業基盤研究(B)「好酸性硫酸還元菌から紐解く始原的微生物の代謝と生息場(研究代表者:加藤真悟、JP24K00747)」、RIKEN TRIPユースケースフィールドオミックスなどによる助成を受けて行われました。
原論文情報
- Shingo Kato, Sachiko Masuda, Arisa Shibata, Takashi Itoh, Mitsuo Sakamoto, Ken Shirasu, Moriya Ohkuma, "Whole-genome sequencing of diverse 351 cultured prokaryotes including as-yet-unsequenced type strains", Genome Research, 10.1101/gr.281026.125
発表者
理化学研究所
バイオリソース研究センター 微生物材料開発室
上級研究員 加藤 真悟(カトウ・シンゴ)
室長 大熊 盛也(オオクマ・モリヤ)
環境資源科学研究センター 植物免疫研究グループ
研究員 増田 幸子(マスダ・サチコ)
グループディレクター 白須 賢(シラス・ケン)
報道担当
理化学研究所 広報部 報道担当
お問い合わせフォーム
